La infección por Candida se ha convertido en un importante problema de salud en todo el mundo. La epidemiología de la candidemia se ha modificado considerablemente por la emergencia de las especies de Candida no-albicans. Esta variación tiene especial importancia en la elección de la profilaxis y tratamiento empírico. Los métodos bioquímicos y los basados en biología molecular presentan limitaciones para la identificación correcta de las especies de Candida. El objetivo de este estudio es demostrar la capacidad del sistema de espectrometría de masas MALDI-TOF para la identificación de estas especies y compararlo con la tecnología utilizada en la actualidad.
MétodosSe incluyeron todos los aislados recogidos durante dos años (n=73) de Candida no-albicans procedentes de muestras invasivas. La identificación se realizó mediante los sistemas Vitek-2 YST y API CAUX. Las identificaciones del MALDI-TOF se hicieron con el sistema Axima Confidence (Shimadzu Corporation), utilizando el software Shimadzu Launchpad y la base de datos SARAMIS (AnagnosTec GmbH). Las discrepancias se resolvieron mediante PCR multiplex LightCycler SeptiFast, PCR específica de C. glabrata y digestión enzimática con BanI del fragmento SADH en los aislados de C. parapsilosis.
ResultadosDe los 73 aislados de Candida no-albicans, los métodos bioquímicos identificaron de forma concluyente 67 a nivel de especie y 6 a nivel de género. El sistema MALDI-TOF obtuvo identificaciones a nivel de especie en todas ellas. La correlación en la especie de todos los aislados estudiados fue del 85,07%, llegando al 94,52% si se estudia la correlación entre la identificación obtenida mediante métodos bioquímicos junto con los métodos empleados para el análisis de las discrepancias. En los aislados de C. parapsilosis, el sistema MALDI-TOF obtuvo una identificación de C. orthopsilosis en tres de ellos, confirmándose por digestión con BanI del fragmento SADH.
ConclusiónEn este estudio se ha demostrado la utilidad de la espectrometría de masas (sistema MALDI-TOF) para dotar al laboratorio de microbiología de una mayor eficiencia y fiabilidad para la identificación a nivel de especie de los aislados de Candida no-albicans. Además de mostrar su posible utilidad para la identificación de especies relacionadas como C. parapsilosis, orthopsilosis y metapsilosis.
Candida infection has become a major health problem worldwide. The epidemiology of Candidaemia has substantially changed by the emergence of the species Candida non-albicans. This variation is particularly important in the choice of prophylaxis and empirical treatment. The methods based on biochemical and molecular biology have limitations for the correct identification of Candida species. The aim of this study is to demonstrate the ability of the MALDI-TOF mass spectrometry for the identification of these species and compare it with the technology used today.
MethodsWe included all isolates collected over 2 years (n=73) of Candida non-albicans from non-invasive samples. The identification was carried out by Vitek-2 systems YST and API CAUX. The MALDI-TOF identifications were made with Confidence Axima system (Shimadzu Corporation) using the Shimadzu Launchpad software and database SARAMIS (AnagnosTec GmbH). Discrepancies were resolved by SeptiFast LightCycler multiplex PCR, specific PCR C. glabrata and enzymatic digestion with BanI SADH fragment in isolates of C. parapsilosis.
ResultsOf the 73 isolates of Candida non-albicans, the biochemical methods conclusively identified 67 to species level and 6 at the genus level. The MALDI-TOF system obtained identifications at the species level in all cases. The correlation in the species of all isolates studied was 85.07%, reaching 94.52% when the correlation was made between the identification obtained by biochemical methods and the methods for the analysis of the discrepancies. In isolates of C. parapsilosis, MALDI-TOF system obtained an identification of C. orthopsilosis. In 3 of them it was confirmed by digestion with BanI SADH fragment.
ConclusionThis study has demonstrated the use of mass spectrometry (MALDI-TOF system) to provide the microbiology laboratory with greater efficiency and reliability to identify isolates of Candida non-albicans to species level. It also shows its potential usefulness in identifying related species, such as C. parapsilosis, metapsilosis and orthopsilosis.
La infección por Candida se ha convertido en los últimos años en un importante problema de salud en todo el mundo1,2, debido a los cambios experimentados en la población de riesgo3. Esta infección se asocia con un aumento en las tasas de morbilidad y mortalidad. Los estudios retrospectivos de cohortes con pacientes con candidemia y diferentes enfermedades de base cifran la mortalidad cruda entre un 30-81% y atribuible 50-71%. En estudios recientes la tasa de mortalidad cruda a las 12 semanas se sitúa en un 35,2%4, correspondiendo las tasas más elevadas a infecciones por Candida no-albicans5,6.
Existen diferencias en la epidemiología de la candidemia entre los diferentes países. En España, la incidencia se sitúa entre 0,76 y 0,81 por 100 ingresos, rango mayor al observado en otros países europeos, EE. UU. y Canadá. Candida spp. es en frecuencia el sexto patógeno aislado en sangre, y la infección por este organismo supone un 10% de todas las infecciones con un número estimado de 4,3 episodios de candidemia por cada 1.000 habitantes2.
Aunque Candida albicans continúa siendo la especie más frecuente, se observa la emergencia de especies de Candida no-albicans, la aparición de especies resistentes a azoles y el desarrollo de resistencias secundarias en aislados previamente sensibles7. Este aumento se ha asociado con el uso de catéteres vasculares y de nutrición parenteral, neoplasia, neutropenia y exposición previa a azoles. C. parapsilosis causa la mayoría de procesos infecciosos debidos a especies no-albicans. En general la elección de profilaxis y recomendaciones terapéuticas se basan en la posible implicación de C. glabrata o C. krusei, resistentes a azoles5,8.
La identificación de levaduras se realiza habitualmente por métodos comerciales basados en la asimilación de carbohidratos como API ID 32C, API CAUX o mediante métodos automatizados como el sistema Vitek ID YST (BioMérieux, Marci L¿Étoile, Francia), así como mediante estudios morfológicos en agar harina de maíz o agar arroz, junto con la utilización de medios cromogénicos diferenciales. Entre los problemas de los métodos de identificación fenotípicos destacan su lentitud, condicionada por el crecimiento del hongo, la existencia de bases de datos limitadas y el gran número de identificaciones incorrectas proporcionadas por estos sistemas1. Recientemente se han desarrollado alternativas basadas en técnicas de ADN como la PCR que han aumentado la rapidez diagnóstica y mejorado la capacidad de diferenciación entre especies. Debido a su elevado coste, mayor tiempo de realización y necesidad de personal experto para su interpretación, están en fase de adaptación a la práctica clínica6.
La importancia de la diferenciación de aislados desde el punto de vista epidemiológico y de la identificación rápida de las levaduras a nivel de especie, demanda un sistema que suponga un avance tecnológico en este campo9. En este contexto, el sistema de espectrometría de masas MALDI-TOF es una herramienta emergente capaz de proporcionar una identificación rápida de especies microbianas a partir de colonias aisladas, siendo incluso capaz de diferenciar a nivel de subespecie, como ha quedado demostrado en numerosos trabajos10–12.
El objetivo de este estudio es demostrar la aplicación del sistema MALDI-TOF en la identificación de especies de Candida no-albicans procedentes de aislados clínicos y comparar los resultados con los obtenidos por los métodos bioquímicos disponibles en la actualidad.
Material y métodosAislados clínicosEn el estudio se incluyeron los 73 aislados de Candida no-albicans obtenidos a partir de muestras invasivas recibidas en un período de dos años, entre mayo de 2008 y mayo 2010, en el Servicio de Microbiología del Complexo Hospitalario Universitario de Santiago de Compostela (CHUS). Las muestras se sembraron en medios de cultivo habituales de acuerdo con la metodología microbiológica convencional y se subcultivaron en agar Sabuoraud con 2% glucosa (Becton dickinson, Heidelberg, Alemania) y en CHROMagar Candida (Becton dickinson, Heidelberg, Alemania) para su identificación presuntiva.
Identificación bioquímicaLa identificación bioquímica se realizó mediante el sistema automatizado Vitek-2 YST (BioMérieux, Marci L¿Étolie, Francia) y cuando el sistema no ofreció una identificación fiable con porcentajes superiores al 95%, se reidentificó mediante API CAUX (BioMérieux, Marci L¿Étolie, Francia).
MALDI-TOF MSTras la incubación de los aislados 48 horas en agar Sabuoraud con 2% glucosa, se transfirieron 2-3 colonias a un tubo de extracción con tapón de rosca de 1,5ml (Eppendorf, Alemania) mezclándose con 0,5ml de etanol absoluto y se centrifugó a 10.000rpm durante 10 minutos. El sedimento resultante se secó al aire y se mezcló con 50 ul de ácido fórmico al 25%. Se depositaron 0,5 ul del sobrenadante sobre la placa de MALDI-TOF MS y se dejó secar a temperatura ambiente. Por último, se añadió 0,5 ul de la matriz ácido 2,5-dihidroxibenzóico (DHB) para la precipitación de las proteínas y péptidos celulares.
Los espectros de picos se generaron con el sistema Axima Confidence (Shimadzu Corporation), utilizando el software Shimadzu Launchpad y la base de datos SARAMIS (AnagnosTec GmbH) para la medida e identificación automáticas. Los porcentajes de confianza en la identificación a nivel de familia, género y especie se generaron por comparación con los superespectros de la base de datos del sistema. Sólo los porcentajes mayores del 90% se consideraron válidos en este estudio. El espectrómetro se calibró externamente utilizando la cepa de Escherichia coli de referencia para el sistema.
Análisis de las discrepanciasReidentificación de los aislados de Candida parapsilosisLa redefinición del grupo taxonómico de C. parapsilosis incluye dos especies adicionales: C. orthopsilosis y C. metapsilosis, incluidas en las bases de datos del sistema MALDI-TOF MS. Para la reidentificación de los aislados de C. parapsilosis se utilizó el método de digestión con BanI del fragmento SADH (secondary alcohol dehydrogenase) descrito por Tavanti et al13.
Reidentificación de los aislados de Candida glabrataRecientemente se ha constatado que fenotípicamente Candida glabrata puede comportarse como Candida nivariensis y Candida bracariensis. Con el fin de asegurar la identificación correcta de esta especie de Candida y para el análisis de resultados discrepantes, se empleó una PCR específica de C. glabrata con los primeros CGL1 y CGL2 descritos previamente14,15.
Identificación genotípica mediante PCR real-time multiplexPara la confirmación de los resultados discrepantes por ambos métodos se utilizó el sistema LightCycler SeptiFast test Mgrade (Roche Diagnostics GmbH), previa lisis mecánica por sistema MagnaLyser (Roche Diagnostics GmbH) y extracción con el sistema automático MagnaPure Compact (Roche Applied Science, GmbH), siguiendo las instrucciones del fabricante. Este sistema permite la identificación de 5 especies de Candida sp. (C. albicans, C. parapsilosis, C. krusei, C. glabrata y C. tropicalis), mediante la amplificación de las regiones ITS (internal transcribed spacer) del ADN.
ResultadosLos métodos bioquímicos identificaron de forma concluyente 67 de los 73 aislados de Candida no-albicans a nivel de especie y 6 a nivel de género. El sistema MALDI-TOF MS obtuvo identificaciones a nivel de especie en todas ellas con un porcentaje superior al 90%.
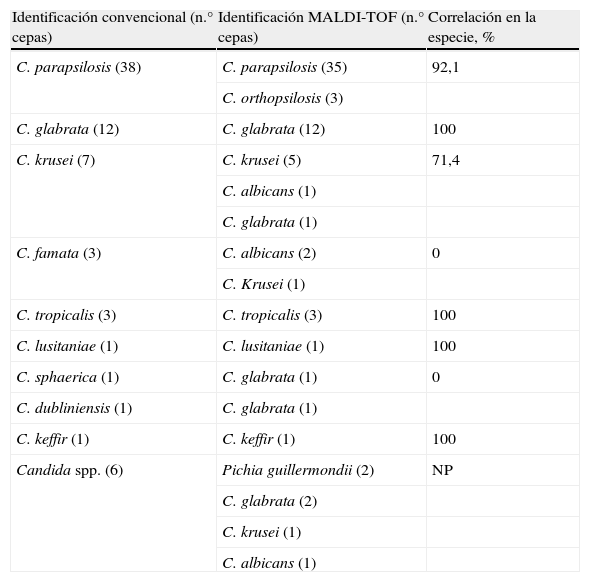
Se obtuvieron resultados concordantes en 35C. parapsilosis; 12C. glabrata; 5C. krusei; 3C. tropicalis; 1C. lusitaniae, y 1 C. kefir. La correlación en la especie de todos los aislados estudiados fue del 85,07%, llegando a un valor del 94,52% si se estudia la correlación entre la identificación obtenida mediante todas las técnicas de confirmación utilizadas respecto al sistema de espectrometría de masas MALDI-TOF (tabla 1).
Comparación de la identificación de 73 Candidas no-albicans mediante métodos microbiológicos convencionales y mediante espectrometría de masas matrix-assisted laser desortion ionization time-of-flight
| Identificación convencional (n.° cepas) | Identificación MALDI-TOF (n.° cepas) | Correlación en la especie, % |
| C. parapsilosis (38) | C. parapsilosis (35) | 92,1 |
| C. orthopsilosis (3) | ||
| C. glabrata (12) | C. glabrata (12) | 100 |
| C. krusei (7) | C. krusei (5) | 71,4 |
| C. albicans (1) | ||
| C. glabrata (1) | ||
| C. famata (3) | C. albicans (2) | 0 |
| C. Krusei (1) | ||
| C. tropicalis (3) | C. tropicalis (3) | 100 |
| C. lusitaniae (1) | C. lusitaniae (1) | 100 |
| C. sphaerica (1) | C. glabrata (1) | 0 |
| C. dubliniensis (1) | C. glabrata (1) | |
| C. keffir (1) | C. keffir (1) | 100 |
| Candida spp. (6) | Pichia guillermondii (2) | NP |
| C. glabrata (2) | ||
| C. krusei (1) | ||
| C. albicans (1) |
NP: no procede.
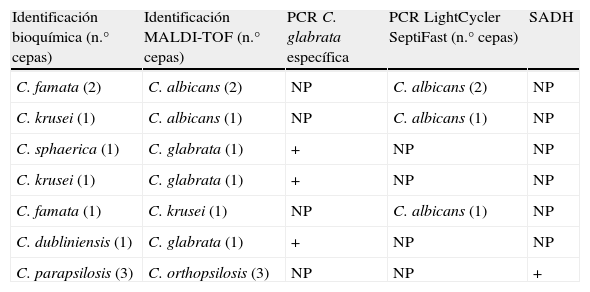
En diez aislados se encontraron discrepancias por ambos métodos. La ausencia de correlación se cifra en el 5,48% correspondientes a dos aislados no confirmados de Pichia guillermondii y otros dos en los que se obtuvo una identificación diferente por los cuatro métodos de confirmación (tabla 2).
Discrepancias obtenidas entre los métodos convencionales y el sistema MALDI-TOF
| Identificación bioquímica (n.° cepas) | Identificación MALDI-TOF (n.° cepas) | PCR C. glabrata específica | PCR LightCycler SeptiFast (n.° cepas) | SADH |
| C. famata (2) | C. albicans (2) | NP | C. albicans (2) | NP |
| C. krusei (1) | C. albicans (1) | NP | C. albicans (1) | NP |
| C. sphaerica (1) | C. glabrata (1) | + | NP | NP |
| C. krusei (1) | C. glabrata (1) | + | NP | NP |
| C. famata (1) | C. krusei (1) | NP | C. albicans (1) | NP |
| C. dubliniensis (1) | C. glabrata (1) | + | NP | NP |
| C. parapsilosis (3) | C. orthopsilosis (3) | NP | NP | + |
NP: no procede.
En los 38 aislados de C. parapsilosis identificados por los métodos convencionales, el sistema MALDI-TOF obtuvo una identificación de C. orthopsilosis en tres de ellos que se confirmaron como tales por el método de digestión con BanI del fragmento SADH.
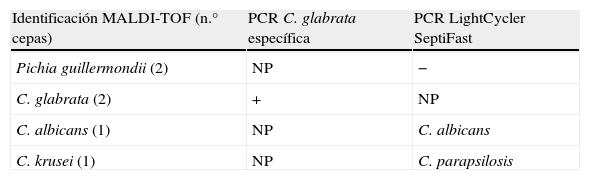
Los resultados de los aislados que bioquímicamente se clasificaron como Candida spp. se muestran en la tabla 3.
Identificación de los aislados Candida spp. a nivel de especie por el sistema MALDI-TOF MS
| Identificación MALDI-TOF (n.° cepas) | PCR C. glabrata específica | PCR LightCycler SeptiFast |
| Pichia guillermondii (2) | NP | − |
| C. glabrata (2) | + | NP |
| C. albicans (1) | NP | C. albicans |
| C. krusei (1) | NP | C. parapsilosis |
NP: no procede.
La identificación correcta y rápida de los hongos patógenos, aislados a partir de muestras clínicas es uno de los objetivos a alcanzar para el manejo correcto del paciente con candidemia y para el control de la infección fúngica invasora. Conociendo la variabilidad en la susceptibilidad a antifúngicos inherente a las diferentes especies de Candida, la correcta identificación a nivel de especie es a menudo crítica para tomar decisiones terapéuticas.
Como se ha demostrado, la combinación de varios sistemas de identificación contribuye a la calidad y eficacia de la identificación llevada a cabo de forma convencional en el laboratorio de la especies de Candida16. Los sistemas basados en la biología molecular presentan limitaciones relacionadas con su complejidad, fundamentalmente debido a la preparación de la muestra, la posibilidad de contaminación ambiental, aplicación limitada sobre muestra clínica directamente, etc. En la práctica, a pesar de su teórica rapidez y de surgir como alternativa a los métodos convencionales fenotípicos, se reservan como métodos confirmatorios11.
En este estudio se ha demostrado la utilidad del sistema MALDI-TOF que es capaz de proporcionar un espectro de picos para la identificación de Candida sp. a nivel de género y especie9. La correlación entre este nuevo método y los métodos disponibles en el laboratorio ha alcanzado un valor mayor al 85%. El hecho de que este valor supere el 90% al combinar los diferentes métodos de confirmación de identificación pone de manifiesto tanto la superioridad del sistema MALDI-TOF, como el elevado número de errores atribuidos a los métodos convencionales empleados en el laboratorio; estos valores de correlación elevados son similares a los obtenidos en estudios previos12. No obstante, los estudios de aplicación de la espectrometría de masas para la identificación de especies fúngicas son más recientes que los llevados a cabo en bacterias, ya que es evidente que para obtener los espectros característicos en el caso de estos microorganismos se necesitan varios pasos previos de preparación de la muestra, que implican la lisis celular y que hacen el proceso más complejo que en el caso de las bacterias. Estudios recientes han demostrado que la fijación con alcohol permite obtener resultados reproducibles, además de favorecer la suspensión celular previa a la disposición de la muestra en la placa de MALDI-TOF. Este sistema comparado con otros métodos de lisis ha demostrado ser el mejor de ellos, resultando un método rápido y sencillo de preparación de muestras fúngicas9.
En nuestro estudio se pone de manifiesto que el uso de los sistemas bioquímicos, puede confundir los aislados de C. famata con C. albicans, no obstante, el número reducido de aislados incluidos en el trabajo refleja la necesidad de estudios posteriores que confirmen este hecho. Además, en concordancia con lo demostrado en otros trabajos17, el MALDI-TOF parece ser un sistema útil para la identificación de especies relacionadas como C. parapsilosis, orthopsilosis y metapsilosis. De los 38 aislados de C. parapsilosis clasificadas por los métodos convencionales, detectó el total de aislados de C. orthopsilosis confirmados posteriormente como tales por digestión enzimática. El interés en la caracterización correcta del grupo «psilosis» no es sólo epidemiológico, sino que es importante debido a las posibles diferencias en los estudios de sensibilidad a antifúngicos. Estas nuevas especies estrechamente relacionadas con C. parapsilosis han mostrado sensibilidades disminuidas a anfotericina B e incluso a las equinocandinas18,19. Del mismo modo se ha atribuido una virulencia menor a C. metapsilosis que a C. parapsilosis y orthopsilosis13,16. No obstante, la prevalencia de estas especies en España es todavía baja con valores que se sitúan entre 1,4-1,7%, como productoras de candidemia18.
Puesto que, este sistema ha demostrado la capacidad de diferenciar entre aislados del grupo «psilosis», podría pensarse en la aplicación de este método para la discriminación de C. glabrata, C. nivariensis y C. bracariensis, fenotípicamente indistinguibles. En los últimos años se ha observado un aumento en su incidencia, mostrando CMI elevadas a azoles y equinocandinas; por ello parece prudente buscar nuevos sistemas que permitan asignar de forma correcta su identificación con el fin de monitorizar estos patógenos con multirresistencia emergentes20,21.
De forma global, la identificación mediante espectrometría de masas presenta varias ventajas fundamentales: sencillez en la preparación de muestra, no necesidad de tinción de gram, escaso volumen, rapidez en la obtención de resultados (once minutos) y el bajo coste a pesar de tratarse de un equipo caro con un precio es comparable al de otros equipos comunes en el laboratorio de microbiología y un coste de material fungible prácticamente nulo10–12. Una limitación de este sistema es que no proporciona datos de susceptibilidad a antimicrobianos, sin embargo, la resistencia a antibióticos depende de la producción de péptidos y proteínas específicas, por lo que la aplicación de los espectrómetros de masas en este campo es una futura posibilidad. Estudios recientes han demostrado la posibilidad y las ventajas de la aplicación del sistema MALDI-TOF sobre muestra clínica y hemocultivo positivo22–24. Existen publicaciones en los que se identificaron de forma correcta el 100% de los aislados de C. albicans. No obstante, en otros trabajos se pone de manifiesto la limitación de este nuevo método en la detección de fungemia por Candida sp.21,25. Probablemente en relación con la baja concentración de microorganismos en sangre que en esta entidad clínica puede ser menor de 100 ufc/ml16.
Trabajos recientes han estudiado la aplicación de la espectrometría de masas en el tipado de C. albicans y C. parapsilosis, obteniéndose una elevada heterogeneidad entre los aislados estudiados, lo que refleja la elevada complejidad biológica de las levaduras y convierte al sistema MALDI-TOF en un complemento de las herramientas de tipado disponibles, importante para conocer los patrones de dispersión de la infección fúngica desde el punto de vista epidemiológico, lo que amplia todavía más las aplicaciones de este nuevo método22.
En el futuro podría plantearse como método previo a la secuenciación del 16S reduciéndose así el coste y tiempo necesarios para la identificación microbiológica. No obstante, en la actualidad esta aplicación pasa por la necesidad de mejora, ampliación y consenso de las bases de datos de los principales patógenos humanos disponibles por el sistema11,12,26.
Conflicto de interesesLos autores declaran no tener ningún conflicto de intereses.