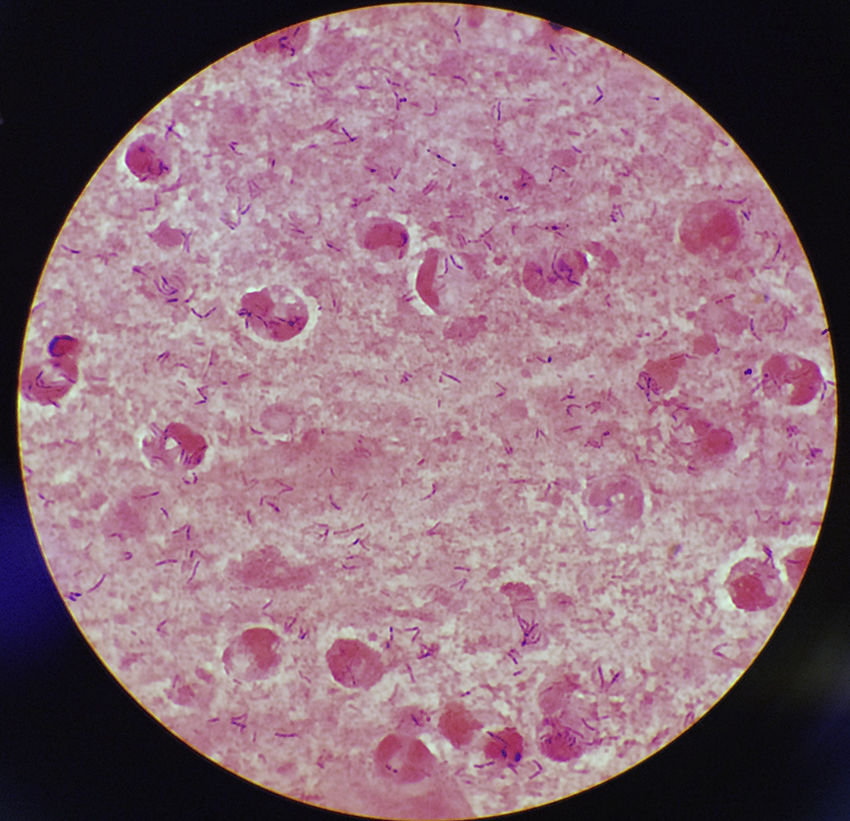
Hoy está universalmente reconocida la renovada y creciente importancia de la patología infecciosa: aparición de nuevos agentes patógenos, de cepas resistentes, de procesos con expresión clínica hasta ahora desconocida, de cuadros de una gran complejidad. Paralelamente, la Microbiología y la Infectología Clínicas han experimentado un gran desarrollo como respuesta al reto planteado por la actual patología infecciosa. Enfermedades Infecciosas y Microbiología Clínica es la Publicación Oficial de la Sociedad Española SEIMC. Cumple con la garantía científica de esta Sociedad, la doble función de difundir trabajos de investigación, tanto clínicos como microbiológicos, referidos a la patología infecciosa, y contribuye a la formación continuada de los interesados en aquella patología mediante artículos orientados a ese fin y elaborados por autores de la mayor calificación invitados por la revista.